Metabolismo
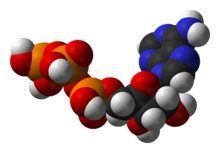
In biochimica il metabolismo (dal greco μεταβολή ossia "cambiamento") è l'insieme delle trasformazioni chimiche che si dedicano al mantenimento vitale all'interno delle cellule degli organismi viventi. Queste reazioni catalizzate da enzimi consentono agli organismi di crescere e riprodursi, mantenere le proprie strutture e rispondere alle sollecitazioni dell'ambiente circostante. La parola "metabolismo" può anche riferirsi a tutte quelle reazioni chimiche che avvengono negli organismi viventi, incluse la digestione e il trasporto di sostanze all'interno delle cellule e tra cellule differenti, nel qual caso la serie di reazioni che avvengono all'interno delle cellule prende il nome di metabolismo intermedio.
Generalità
[modifica | modifica wikitesto]Il metabolismo è generalmente diviso in due categorie: catabolismo, che disgrega la materia organica e produce l'energia attraverso la respirazione cellulare e l'anabolismo che utilizza l'energia per costruire i vari componenti delle cellule, come le proteine e gli acidi nucleici.
Le reazioni chimiche del metabolismo sono organizzate in vie metaboliche, in cui una sostanza chimica subisce un processo di trasformazione attraverso una serie di passi in un'altra sostanza, grazie a una serie di enzimi. Gli enzimi sono fondamentali per il metabolismo poiché permettono agli organismi di compiere le reazioni chimiche volute, che necessitano di tempi di reazione che non permetterebbero la loro esecuzione spontanea. Gli enzimi agiscono come catalizzatori consentendo alle reazioni di procedere più rapidamente. Essi permettono anche la regolazione delle vie metaboliche in risposta ai cambiamenti nel contesto della cellula o ai segnali provenienti da altre cellule.
Il sistema metabolico di un particolare organismo determina quali sostanze rappresenteranno per lui un nutrimento e quali un veleno. Ad esempio, alcuni procarioti utilizzano solfuro di idrogeno come nutriente che, tuttavia, è tossico per altri animali.[1]
Una caratteristica particolare del metabolismo è la somiglianza dei componenti e delle vie metaboliche di base tra le specie viventi, anche molto diversi tra di loro.[2] Per esempio, l'insieme di acidi carbossilici che sono conosciuti come gli intermedi del ciclo dell'acido citrico sono presenti in tutti gli organismi noti, essendo stati riscontrati in specie diverse come il batterio unicellulare Escherichia coli e nei grandi organismi multicellulari come gli elefanti.[3] Queste somiglianze suggeriscono che le vie metaboliche siano probabilmente apparse agli inizi della storia evolutiva e si sono conservati per via della loro efficacia.[4][5]
Principali composti chimici
[modifica | modifica wikitesto]
La maggior parte delle strutture che compongono gli animali, le piante e i microbi sono realizzate grazie a tre classi molecolari di base: amminoacidi, carboidrati e lipidi (chiamati"grassi"). Poiché queste molecole sono essenziali per la vita, la maggior parte delle reazioni metaboliche si concentra sulla sintesi di queste molecole che serviranno per la costruzione delle cellule e dei tessuti. Queste molecole biochimiche possono essere unite per formare polimeri, quali DNA e proteine, macromolecole essenziali della vita.
| Tipo di molecola | Nome della forma monomerica | Nome della forma polimerica | Esempi di forme polimeriche |
|---|---|---|---|
| Amminoacido | Amminoacidi | Proteine (chiamate anche polipeptidi) | Proteine fibrose, proteine globulari |
| Carboidrati | Monosaccaridi | Polisaccaridi | Amido, glicogeno e cellulosa |
| Acidi nucleici | Nucleotide | Polinucleotide | DNA e RNA |
Amminoacidi e proteine
[modifica | modifica wikitesto]Le proteine sono composte da amminoacidi disposti in una catena lineare unita da legami peptidici. Molte proteine sono enzimi che catalizzano le reazioni chimiche proprie del metabolismo. Altre proteine hanno funzioni strutturali o meccaniche, come quelle che formano il citoscheletro, un sistema strutturale che mantiene la forma della cellula.[6] Le proteine rivestono un ruolo importante anche nella segnalazione cellulare, nella risposta immunitaria, nell'adesione cellulare, nel trasporto attivo attraverso le membrane e nel ciclo cellulare.[7]
Gli amminoacidi contribuiscono al metabolismo energetico cellulare fornendo una fonte di carbonio in ingresso nel ciclo dell'acido citrico (ciclo degli acidi tricarbossilici),[8] specialmente quando una fonte primaria di energia, come il glucosio, risulta scarsa o quando la cellula subisce uno stress metabolico.[9]
Lipidi
[modifica | modifica wikitesto]I lipidi sono il gruppo più eterogeneo di sostanze biochimiche. La loro principale funzione è quello di elementi strutturali che formano parte delle membrane biologiche, sia interne sia esterne, come la membrana cellulare, oppure possono essere utilizzati come fonte di energia.[7] I lipidi sono generalmente definiti come molecole biologiche idrofobe o anfipatiche ma si dissolvono in solventi organici quali benzene o cloroformio.[10] I grassi sono un grande gruppo di composti che contengono acidi grassi e glicerolo; una molecola di glicerolo collegato a tre esteri di acidi grassi è chiamato trigliceride.[11] Esistono diverse varianti di questa struttura di base, tra cui dorsali alternative come la sfingosina negli sfingolipidi e gruppi idrofili come il fosfato nei fosfolipidi. Steroidi, come il colesterolo, rappresentano un'altra grande classe di lipidi.[12]
Carboidrati
[modifica | modifica wikitesto]
I carboidrati sono aldeidi o chetoni, con molti gruppi idrossile collegati, che possono esistere come catene lineari o ad anello; quelli a catena lineare sono molto più reattivi nel senso della glicazione (tuttavia almeno per quanto riguarda glucosio e fruttosio l'isomero lineare rappresenta meno dell'1% del composto totale). I carboidrati sono le molecole biologiche più importanti e assecondano a numerosi ruoli, ad esempio la conservazione e il trasporto dell'energia (amido, glicogeno) e la sintesi di componenti strutturali (cellulosa nelle piante, chitina negli animali).[7] Le unità di base dei carboidrati sono chiamati monosaccaridi e includono il galattosio, il fruttosio e soprattutto il glucosio. I monosaccaridi possono essere collegati insieme per formare i polisaccaridi in modi diversi quasi illimitati.[13]
Nucleotidi
[modifica | modifica wikitesto]I due acidi nucleici, il DNA e l'RNA, sono polimeri di nucleotidi. Ogni nucleotide è composto da un fosfato collegato a un gruppo zuccherino di ribosio o desossiribosio che è a sua volta collegato a una base azotata. Gli acidi nucleici sono fondamentali per la conservazione e per l'uso della informazione genetica e per la sua interpretazione grazie ai processi di trascrizione e biosintesi delle proteine.[7] Queste informazioni sono protette da meccanismi di riparazione del DNA e trasmesse attraverso la replicazione del DNA. Molti virus possiedono un genoma di RNA, come l'HIV, che utilizza la trascrizione inversa per creare uno stampo di DNA dal proprio genoma virale a RNA.[14] L'RNA contenuto nei ribozimi, come spliceosomi e ribosomi, è simile agli enzimi e come loro è in grado di catalizzare reazioni chimiche. I nucleosidi individuali sono realizzati collegando una base azotata a uno zucchero ribosio. Queste basi sono anelli eterociclici contenenti azoto e classificati come purine o pirimidine. I nucleotidi agiscono anche come coenzimi nelle reazioni metaboliche di trasferimento.[15]
Coenzimi
[modifica | modifica wikitesto]Il metabolismo coinvolge una vasta gamma di reazioni chimiche, ma la maggior parte di esse rientrano in alcuni tipi fondamentali che comportano il trasferimento di gruppi funzionali di atomi e dei loro legami all'interno di molecole.[16] Questa chimica comune permette alle cellule di utilizzare un piccolo insieme di metaboliti intermedi per trasportare composti chimici tra diverse reazioni.[15] Questi intermedi di trasferimento sono chiamati coenzimi. Ogni reazione che coinvolge gli intermedi di trasferimento è effettuata da un particolare coenzima, che funge da substrato per alcuni enzimi prodotti e per alcuni enzimi consumati. Pertanto, questi coenzimi vengono continuamente sintetizzati, consumati e riciclati.[17] La loro quantità esistente è modulata dall'effetto feedback, ovvero dal rapporto tra substrato e prodotto.
Un coenzima molto importante è l'adenosina trifosfato (ATP), definito come "la moneta energetica" universale delle cellule. Questo nucleotide viene utilizzato per trasferire energia chimica tra diverse reazioni. Nelle cellule è presente soltanto una piccola quantità di ATP, ma esso viene continuamente rigenerato.[17] L'ATP funge da ponte tra il catabolismo e l'anabolismo. Il catabolismo rompe le molecole, mentre l'anabolismo le mette insieme. Le reazioni cataboliche generano ATP e le reazioni anabolizzanti lo consumano. L'ATP serve anche come portatore di gruppi fosfati nelle reazioni di fosforilazione.
La vitamina A è un composto organico, necessario in piccole quantità, che non può essere sintetizzato dalle cellule. Nella nutrizione umana, la maggior parte delle vitamine assolve il compito di coenzima dopo essere state modificate; per esempio, tutte le vitamine idrosolubili sono fosforilate o sono accoppiate ai nucleotidi quando vengono utilizzate nelle cellule.[18] La nicotinammide adenina dinucleotide (NAD+), un derivato della vitamina B3 (niacina), è un coenzima importante che funge da accettore di idrogeno. Centinaia di tipi distinti di deidrogenasi rimuovono gli elettroni dai loro substrati e riducono il NAD+ in NADH. Questa forma ridotta del coenzima è quindi un substrato per qualsiasi riduttasi per le cellule che necessitano di ridurre i loro substrati.[19] Nella cellula, il NAD+ esiste in due forme correlate, NADH e NADPH. La forma NAD+/NADH è più importante nelle reazioni cataboliche, mentre quella NADP+/NADPH viene utilizzata nelle reazioni anabolizzanti.
Minerali e cofattori
[modifica | modifica wikitesto]Anche gli elementi inorganici giocano un ruolo fondamentale nel metabolismo; alcuni sono abbondanti (ad esempio sodio e potassio), mentre altri assolvono alla loro funzione a concentrazioni minime. Circa il 99% della massa di un mammifero è costituita da carbonio, azoto, calcio, sodio, cloro, potassio, idrogeno, fosforo, ossigeno e zolfo.[20] Composti organici (proteine, lipidi e carboidrati) contengono la maggior parte del carbonio e dell'azoto; la maggior parte dell'ossigeno e dell'idrogeno è presente sotto forma di acqua.[20] Si consideri che buona parte degli ormoni (in particolare gli steroidei e i peptidici) inducono (tramite i recettori che sono vere e proprie pompe ioniche) una variazione delle quantità di sali disciolti nel citoplasma, tale variazione determina effetti sull'attività della cellula; altri ormoni, quali l'adrenalina, agiscono senza influenzare la pressione osmotica, mediante messaggeri intracellulari ("secondi messaggeri").
Gli abbondanti elementi inorganici agiscono come elettroliti ionici. Gli ioni più importanti sono il sodio, potassio, calcio, magnesio, cloruro, fosfato e idrogenocarbonato. Il mantenimento di precisi gradienti ionici attraverso le membrane cellulari permette di mantenere la corretta pressione osmotica e giusti valori di pH.[21] Gli ioni sono anche fondamentali per i nervi e per la funzione muscolare: infatti il meccanismo dei potenziali d'azione, in questi tessuti, viene realizzato grazie allo scambio di elettroliti tra il liquido extracellulare e il citosol, il fluido interno alla cellula.[22] Gli elettroliti possono entrare e uscire dalle cellule grazie a proteine chiamate canali ionici della membrana cellulare. Ad esempio, la contrazione muscolare dipende dal movimento del calcio, del sodio e del potassio attraverso i canali ionici della membrana cellulare e dei tuboli trasversi.[23]
I metalli di transizione sono solitamente presenti negli organismo come oligoelementi, con lo zinco e il ferro che sono quelli più abbondanti.[24][25] Questi metalli sono utilizzati in alcune proteine come cofattori e sono essenziali per l'attività di alcuni enzimi quali i catalasi e le proteine per il trasporto dell'ossigeno, come l'emoglobina.[26] I cofattori metallici sono legati strettamente a siti specifici nelle proteine; sebbene i cofattori enzimatici possono essere modificati durante la catalisi, essi tornano sempre allo stato originale alla fine della reazione catalizzata. I micronutrienti metallici sono oggetto di trasportatori specifici e si legano alle proteine di riserva, come la ferritina o metallotioneina, quando non vengono utilizzati.[27][28]
Catabolismo
[modifica | modifica wikitesto]Il catabolismo è l'insieme dei processi metabolici in grado di abbattere le grandi molecole. Questi includono la scomposizione e l'ossidazione delle molecole assunte con l'alimentazione. Lo scopo delle reazioni cataboliche è quello di fornire l'energia e i componenti necessari per le reazioni anabolizzanti. L'esatta natura di queste reazioni cataboliche differisce da organismo a organismo e gli stessi organismi possono essere classificati in base alle loro fonti di energia, come mostrato nella tabella sottostante. Le molecole organiche sono utilizzate come fonte di energia dagli organotrofi, mentre i litotrofi utilizzano substrati inorganici e fototrofi per catturare la luce solare come energia chimica. Tuttavia tutte queste diverse forme di metabolismo dipendono da reazioni di ossidoriduzione che comportano il trasferimento di elettroni da molecole donatrici, quali molecole organiche, acqua, ammoniaca, solfuro di idrogeno, a molecole accettori come ossigeno, nitrato o solfato.[29] Negli animali queste reazioni coinvolgono molecole organiche complesse che vengono metabolizzate a molecole più semplici, come l'anidride carbonica e l'acqua. Negli organismi fotosintetici, come piante e cianobatteri, queste reazioni di trasferimento degli elettroni non rilasciano energia, ma vengono utilizzate come un modo per immagazzinare quella assorbita dalla luce solare.[30]
| Sorgente di energia | Luce solare | Foto- | -trofi | ||
| Molecole preformate | Chemo- | ||||
| Donatori di elettroni | Composti organici | Organo- | |||
| Composti inorganici | Lito- | ||||
| Sorgente di carbonio | Composti organici | Etero- | |||
| Composti inorganici | Auto- | ||||
Il gruppo più comune di reazioni cataboliche negli animali può essere suddiviso in tre fasi principali. Nella prima, grandi molecole organiche come proteine, polisaccaridi o lipidi sono digeriti nei loro componenti più piccoli all'esterno delle cellule. Successivamente queste molecole più piccole sono prese dalle cellule e convertite in molecole ancora più piccole, di solito in coenzima A, rilasciando una certa energia. Infine il gruppo acetile del CoA viene ossidato in acqua e biossido di carbonio nel ciclo dell'acido citrico e nella catena di trasporto degli elettroni, rilasciando l'energia immagazzinata riducendo il coenzima nicotinammide adenina dinucleotide (NAD+) in NADH.
Digestione
[modifica | modifica wikitesto]Le macromolecole come l'amido, la cellulosa o le proteine, non possono essere rapidamente assorbite dalle cellule e devono essere scomposte in composti più piccoli prima di poter essere utilizzate nel metabolismo cellulare. Diversi enzimi si occupano di svolgere questo compito e comprendono le proteasi che digeriscono le proteine in amminoacidi, così come le glicoside idrolasi che digeriscono i polisaccaridi in zuccheri semplici, noti come monosaccaridi.
I microbi semplicemente secernono enzimi digestivi nell'ambiente circostante,[31][32] mentre gli animali li secernono esclusivamente da cellule specializzate presenti nei loro visceri.[33] Gli aminoacidi o gli zuccheri creati da questi enzimi extracellulari vengono poi inseriti nelle cellule grazie a proteine di trasporto attivo.[34][35]
Energia da composti organici
[modifica | modifica wikitesto]
Il catabolismo dei carboidrati consiste nella loro ripartizione in unità più piccole. I carboidrati vengono generalmente assunti nelle cellule una volta che sono stati digeriti in monosaccaridi.[36] Una volta all'interno, la principale via di ripartizione è la glicolisi, dove gli zuccheri, come il glucosio e il fruttosio, vengono convertiti in piruvato e viene generato ATP.[37] Il piruvato è un intermedio in diverse vie metaboliche, ma la maggior parte viene convertito in acetil-CoA che alimenta il ciclo dell'acido citrico. Sebbene un certo numero di ATP vengano sintetizzati nel ciclo dell'acido citrico, il prodotto più importante è il NADH, che è costituito da NAD+ dall'ossidazione dell'acetil-CoA. Questa reazione rilascia anidride carbonica come prodotto di scarto. In condizioni anaerobiche, la glicolisi produce lattato, attraverso l'enzima l-lattato deidrogenasi re-ossida il NADH in NAD+ per il suo riutilizzo nella glicolisi. Un percorso alternativo per la degradazione del glucosio è la via dei pentoso fosfati, che riduce il coenzima NADPH e produce pentosi come il ribosio, il componente di zucchero degli acidi nucleici.
I grassi sono catalizzati per idrolisi di acidi grassi liberi e glicerolo. Il glicerolo entra nella glicolisi e gli acidi grassi sono scomposti per beta ossidazione per rilasciare acetil-CoA, che poi viene immessa nel ciclo dell'acido citrico. Gli acidi grassi rilasciano più energia durante l'ossidazione rispetto ai carboidrati perché quest'ultimi contengono più ossigeno nelle loro strutture. Gli steroidi vengono anche scomposti da alcuni batteri in un processo simile alla beta ossidazione comportando il rilascio di notevoli quantità di acetil-CoA, propionil-CoA e piruvato, che possono essere utilizzati dalla cellula per produrre energia. Mycobacterium tuberculosis può anche vivere grazie al lipide colesterolo come unica fonte di carbonio e i geni coinvolti nella via di utilizzo del colesterolo sono importanti durante le varie fasi del ciclo di infezione di questo batterio responsabile della tubercolosi.[38]
Gli aminoacidi sono utilizzati per sintetizzare le proteine e altre biomolecole o ossidati di urea e anidride carbonica come fonte di energia.[39] Il percorso di ossidazione inizia con la rimozione del gruppo amminico grazie a una transaminasi. Il gruppo amminico viene alimentato nel ciclo dell'urea, lasciando uno scheletro di carbonio deaminato sotto forma di un chetoacido. Molti di questi chetoacidi sono intermedi del ciclo dell'acido citrico, per esempio l'acido 2-chetoglutarico permette la deaminazione di forme di acido glutammico.[40] Gli aminoacidi glicogenici possono anche essere convertiti in glucosio, attraverso la gluconeogenesi.[41]
Trasformazioni energetiche
[modifica | modifica wikitesto]Fosforilazione ossidativa
[modifica | modifica wikitesto]Grazie alla fosforilazione ossidativa, gli elettroni rimossi dalle molecole organiche vengono trasferiti all'ossigeno e l'energia rilasciata è utilizzata per sintetizzare ATP. Questo processo viene svolto negli eucarioti da una serie di proteine nelle membrane mitocondriali che formano la catena di trasporto degli elettroni. Nei procarioti, queste proteine si trovano nella membrana interna della cellula.[42] Tali proteine utilizzano l'energia rilasciata dal passaggio degli elettroni dalle molecole ridotte, come NADH, per pompare protoni attraverso la membrana.[43]
Il pompaggio dei protoni (ovvero dello ione idrogeno+) fuori dei mitocondri crea una differenza, attraverso la membrana, della concentrazione dei protoni stessi, andando quindi a instaurare un gradiente elettrochimico.[44] Il gradiente agisce come una forza che spinge i protoni nuovamente all'interno dei mitocondri, grazie all'enzima ATP sintasi. Il flusso di protoni fa ruotare la subunità, facendo sì che il sito attivo del dominio sintasi cambi di forma e fosforilizzi l'adenosina difosfato, trasformandola in ATP.[17]
Energia da composti inorganici
[modifica | modifica wikitesto]Il chemiolitotrofismo è un tipo di metabolismo utilizzato dai procarioti grazie al quale essi si procurano l'energia dalla ossidazione dei composti inorganici. Questi organismi possono utilizzare l'idrogeno,[45] i composti solforati ridotti (come il solfuro, l'acido solfidrico e tiosolfato),[1] l'ossido ferroso[46] o l'ammoniaca[47] come fonti di potere riducente e ottenere energia dall'ossidazione di questi composti con accettori di elettroni come l'ossigeno o il nitrito.[48] Questi processi microbici sono importanti nei cicli biogeochimici globali come l'acetogenesi, la nitrificazione e la denitrificazione e sono fondamentali per la fertilità del suolo.[49][50]
Energia dalla luce
[modifica | modifica wikitesto]L'energia proveniente dalla luce del sole viene catturata dalle piante, dai cianobatteri, dai batteri viola, dai chlorobi e da alcuni protisti. Questo processo viene spesso accoppiato alla conversione dell'anidride carbonica in composti organici, come parte della fotosintesi. I processi di cattura dell'energia e di successivo fissaggio al carbonio possono tuttavia operare separatamente nei procarioti, così come i batteri viola e verdi possono utilizzare la luce solare come fonte di energia, mentre smistano la fissazione del carbonio e la fermentazione dei composti organici.[51][52]
In molti organismi la captazione dell'energia solare è simile, in linea di principio, alla fosforilazione ossidativa, in quanto comporta l'immagazzinamento dell'energia come gradiente di concentrazione di protoni e, quindi, questa forza motrice protonica spinge la sintesi di ATP.[17] Gli elettroni necessari per condurre questa catena di trasporto provengono dal centro di reazione fotosintetico o dalle rodopsine. I centri di reazione sono classificati in due tipi a seconda della tipologia di pigmento fotosintetico presente; mentre la maggior parte dei batteri fotosintetici ne possiede uno soltanto, le piante e i cianobatteri ne hanno due.[53]
Nelle piante, alghe e cianobatteri, il fotosistema II utilizza l'energia luminosa per rimuovere gli elettroni dall'acqua, liberando ossigeno come prodotto di scarto. Gli elettroni quindi fluiscono al plastochinolo-plastocianina reduttasi, che utilizza la loro energia per pompare protoni attraverso la membrana tilacoide nel cloroplasto.[17] Questi protoni si muovono indietro attraverso la membrana come guidati dall'ATP sintasi. Gli elettroni quindi fluiscono attraverso il fotosistema I e possono essere o utilizzati per ridurre il coenzima NADP+ per l'uso nel ciclo di Calvin o riciclati per un'ulteriore produzione di ATP.[54]
Anabolismo
[modifica | modifica wikitesto]L'anabolismo è l'insieme dei processi metabolici costruttivi dove l'energia rilasciata dal catabolismo viene utilizzata per sintetizzare molecole complesse. In generale, le molecole complesse che compongono le diverse strutture cellulari sono costituite da piccoli e semplici precursori. L'anabolismo prevede tre fasi fondamentali. In primo luogo, la produzione di precursori come aminoacidi, monosaccaridi, isoprenoidi e nucleotidi, dall'altro, la loro attivazione in forme reattive che utilizzano energia da ATP e, in terzo luogo, l'assemblaggio di tali precursori in molecole complesse quali proteine, polisaccaridi, lipidi e acidi nucleici.
Gli organismi si differenziano per il numero delle molecole che le loro cellule possono sintetizzare per sé stessi. Gli organismi autotrofi, come le piante, possono realizzare molecole organiche complesse, come polisaccaridi e proteine da molecole semplici come l'anidride carbonica e l'acqua. Gli eterotrofi, d'altra parte, richiedono una fornitura esterna di sostanze più complesse, come monosaccaridi e aminoacidi, per la produzione di queste molecole complesse. I microrganismi possono essere ulteriormente classificati per l'ultima fonte della loro energia: i fotoautotrofi e i fotoeterotrofi ottengono energia dalla luce, mentre i chemioautotrofi e chemocheterotrofi la ottengono da reazioni di ossidazione inorganiche.[senza fonte]
Fissazione del carbonio
[modifica | modifica wikitesto]La fotosintesi è la sintesi dei carboidrati per mezzo della luce solare e dell'anidride carbonica (CO2). Nelle piante, nei cianobatteri e nelle alghe, la fotosintesi ossigenica divide le molecole d'acqua, producendo ossigeno come prodotto di scarto. Questo processo utilizza ATP e NADPH prodotto dai centri di reazione fotosintetici, come sopra descritto, per convertire la CO2 in 3-fosfoglicerato, che può poi essere convertito in glucosio. Questa reazione di fissazione del carbonio è permessa grazie all'enzima ribulosio-bisfosfato carbossilasi, parte del ciclo di Calvin-Benson.[55] Tre tipi diversi di fotosintesi si possono verificare: fotosintesi C3, C4 e CAM. Queste tre differiscono per la via che porta l'anidride carbonica al ciclo di Calvin, nella C3 la CO2 si fissa direttamente, mentre nel C4 e CAM la CO2 viene incorporata prima in altri composti, come adattamenti per affrontare la luce solare intensa e condizioni di asciutto.[56]
Nei procarioti fotosintetici i meccanismi di fissazione del carbonio sono più diversificati. Qui, l'anidride carbonica può essere fissata dal ciclo di Calvin-Benson, un ciclo invertito dell'acido citrico[57] o dalla carbossilazione di acetil-CoA.[58][59] I procarioti chemioautotrofi fissano anch'essi la CO2 grazie al ciclo di Calvin-Benson, ma utilizzano l'energia da composti inorganici per innescare la reazione.[60]
Carboidrati e glicani
[modifica | modifica wikitesto]Nell'anabolismo dei carboidrati, gli acidi organici semplici possono essere convertiti in monosaccaridi, come il glucosio, e quindi utilizzati per assemblare polisaccaridi come l'amido. La generazione di glucosio da composti come il piruvato, il lattato, il glicerolo, il glicerato 3-fosfato e gli aminoacidi è chiamato gluconeogenesi. La gluconeogenesi converte il piruvato in glucosio-6-fosfato con una serie di prodotti intermedi, molti dei quali sono condivisi con la glicolisi.[37] Tuttavia, questa via non è semplicemente l'inverso della glicolisi, infatti molte reazioni sono catalizzate da enzimi non glicolitici, la cui presenza è modulata dall'effetto feedback. Questo è importante in quanto consente la formazione e la regolamentazione del glucosio a parte, impedendo che entrambi i percorsi vengano eseguiti contemporaneamente in un ciclo futile.[61][62]
Anche se i lipidi sono un modo comune di immagazzinare energia, nei vertebrati come gli esseri umani, gli acidi grassi non possono essere convertiti in glucosio attraverso la gluconeogenesi, come questi organismi non possono convertire acetil-CoA in piruvato; le piante sono in grado di farlo, ma gli animali non dispongono del meccanismo enzimatico necessario.[63] Come risultato, dopo un lungo periodo di affamamento i vertebrati devono produrre corpi chetonici dagli acidi grassi per sostituire il glucosio nei tessuti poiché il cervello non può metabolizzarli.[64] Altri organismi come piante e batteri risolvono il problema utilizzando il ciclo metabolico gliossilato, che bypassa la decarbossilazione nel ciclo dell'acido citrico e permette la trasformazione di acetil-CoA in ossalacetato, dove può essere utilizzato per la produzione di glucosio.[63][65]
I polisaccaridi e i glicani sono fatti da sequenze aggiunte di monosaccaridi da glicosiltrasferasi grazie a un donatore di glucosio, come l'uridina difosfoglucosio (UDP-glucosio) a un gruppo accettore ossidrile su un polisaccaride. Come uno dei gruppi idrossilici sull'anello del substrato può essere un accettore, i polisaccaridi prodotti possono avere strutture lineari o ramificate.[66] I polisaccaridi prodotti possono avere loro stessi funzioni strutturali o metaboliche, o essere trasferiti ai lipidi e proteine grazie a enzimi chiamati oligosaccariltrasferasi.[67][68]
Acidi grassi, isoprenoidi e steroidi
[modifica | modifica wikitesto]
Gli acidi grassi vengono prodotti grazie alla sintesi degli acidi grassi che polimerizzano e quindi riducono le unità acetil-CoA. Le catene acide negli acidi grassi sono estese da un ciclo di reazioni che aggiungono il gruppo acile, ridurlo a un alcool, disidratarlo a un gruppo di alcheni e poi ridurlo nuovamente a un gruppo alcano. Gli enzimi della biosintesi degli acidi grassi sono suddivisi in due gruppi: negli animali e nei funghi tutte le reazioni di sintesi di acido grasso sono svolte da una singola proteina multifunzionale di tipo I,[69] nei plastidi vegetali e nei batteri un enzima separato di tipo II compie ogni fase del percorso.[70][71]
I terpeni e gli isoprenoidi sono una grande classe di lipidi che includono i carotenoidi e formano la più grande classe dei vegetali prodotti naturali.[72] Questi composti sono sintetizzati dall'assemblamento e dalla modifica delle unità di isoprene donate dai precursori reattivi isopentenil pirofosfato e dimetilallil pirofosfato.[73] Questi precursori possono essere realizzati in modi diversi. Negli animali e negli archeobatteri, la via metabolica dell'acido mevalonico produce questi composti dall'acetil-CoA,[74] mentre nelle piante e nei batteri la via metabolica del metileritritolo fosfato utilizza piruvato e gliceraldeide-3-fosfato come substrati.[73][75] Una reazione importante che utilizza questi donatori è la biosintesi degli steroidi. Qui, le unità di isoprene sono unite insieme per fare squalene per poi essere ripiegate a formare una serie di anelli per creare il lanosterolo.[76] Il lanosterolo poi può essere convertito in altri steroidi, come il colesterolo e l'ergosterolo.[76][77]
Proteine
[modifica | modifica wikitesto]Organismi variano nella loro capacità di sintetizzare i 20 aminoacidi comuni. La maggior parte dei batteri e le piante possono sintetizzarli tutti venti, ma i mammiferi possono solo sintetizzare gli undici aminoacidi non essenziali, così i nove amminoacidi essenziali devono essere ottenuti dall'alimentazione.[7] Alcuni parassiti semplici, come il batterio Mycoplasma pneumoniae, sono totalmente privi della sintesi degli aminoacidi e devono assimilarli direttamente dai loro ospiti.[78] Tutti gli amminoacidi sono sintetizzati da prodotti intermedi della glicolisi, dal ciclo dell'acido citrico o dalla via dei pentoso fosfati. L'azoto viene fornito dal glutammato e glutammina. La sintesi degli aminoacidi dipende dalla formazione dell'alfa-cheto acido appropriato, che viene poi transaminato per formare un amminoacido.[79]
Gli aminoacidi uniti in una catena di legami peptidici formano le proteine. Ogni proteina possiede una sequenza unica di residui aminoacidici che rappresenta la sua struttura primaria. Così come le lettere dell'alfabeto possono essere combinate per formare una varietà quasi infinita di parole, gli aminoacidi possono essere collegati in varie sequenze per formare una grande varietà di proteine. Le proteine sono costituite da aminoacidi che sono stati attivati dal fissaggio a una molecola di RNA transfer tramite un legame estere. Questo precursore-tRNA viene prodotto in una reazione ATP-dipendente effettuata da un amminoacil-tRNA sintetasi.[80] Questo tRNA è quindi un substrato per il ribosoma, che unisce l'amminoacido alla catena proteica, utilizzando la sequenza delle informazioni contenute nell'RNA messaggero.[81]
Sintesi dei nucleotidi e recupero
[modifica | modifica wikitesto]I nucleotidi vengono sintetizzati grazie agli amminoacidi, all'anidride carbonica e all'acido formico in percorsi che richiedono grandi quantità di energia metabolica.[82] Di conseguenza, la maggior parte degli organismi dispongono di sistemi efficaci per mantenere i nucleotidi preformati.[82][83] Le purine sono sintetizzate come nucleosidi (basi allegata al ribosio).[84] Sia l'adenina sia la guanina sono sintetizzate dal precursore nucleoside inosina monofosfato, che viene, a sua volta, sintetizzato utilizzando atomi degli amminoacidi. Le pirimidine, d'altra parte, sono sintetizzate dall'acido orotico, che è formato da glutammina e aspartato.[85]
Xenobiotici e metabolismo ossidoriduttivo
[modifica | modifica wikitesto]Tutti gli organismi sono costantemente esposti a composti che non possono utilizzare come alimenti e che risulterebbero dannosi se si accumulassero nelle cellule, in quanto non possiedono alcuna funzione metabolica. Questi composti potenzialmente dannosi sono detti xenobiotici.[86] Gli xenobiotici, quali le droghe sintetiche, i farmaci, i veleni naturali e gli antibiotici, vengono metabolizzati da una serie di enzimi specifici. Negli esseri umani, essi includono il citocromo P450,[87] il glucuronosiltransferasi,[88] e glutatione S-transferasi.[89] Questo sistema consiste in tre azioni eseguite dagli enzimi, la prima consiste nell'ossidazione dei xenobiotici (fase I) con la successiva coniugazione di gruppi idrosolubili in una molecola (fase II). Gli xenobiotici idrosolubili modificati possono quindi essere espulsi dalle cellule e, negli organismi multicellulari, possono essere ulteriormente metabolizzati prima di essere escreti (fase III). Nell'ecologia queste reazioni sono particolarmente importanti per la biodegradazione microbica degli inquinanti e per il biorisanamento di terreni contaminati.[90] Molte di queste reazioni microbiche vengono condivise con gli organismi multicellulari, ma a causa della incredibile diversità di tipi di microbi questi organismi sono in grado di affrontare una gamma molto più ampia di xenobiotici rispetto agli organismi pluricellulari e sono anche in grado di degradare gli inquinanti organici persistenti come i composti organoclorurati.[91]
Un problema correlato per gli organismi aerobici è lo stress ossidativo.[92] Infatti i processi della fosforilazione ossidativa e la formazione di legami disolfuro durante il ripiegamento proteico producono specie reattive dell'ossigeno come il perossido di idrogeno.[93] Questi ossidanti dannosi vengono rimossi dai metaboliti antiossidanti, come il glutatione e gli enzimi quali catalasi e perossidasi.[94][95]
Termodinamica di organismi viventi
[modifica | modifica wikitesto]Gli organismi viventi devono obbedire alle leggi della termodinamica che descrivono il trasferimento di calore e lavoro. Il secondo principio della termodinamica afferma che in ogni sistema chiuso, la quantità di entropia (disordine) non può diminuire. Anche se gli organismi viventi più complessi sembrano contraddire questa legge, la vita è possibile in quanto tutti gli organismi sono sistemi aperti che scambiano materia ed energia con l'ambiente circostante. In questo modo le specie viventi non si trovano in equilibrio termodinamico, ma sono invece sistemi dissipativi che mantengono il loro stato di elevata complessità comportando un maggiore incremento dell'entropia dei loro ambienti.[96] Il metabolismo di una cellula ottiene questo accoppiando i processi spontanei del catabolismo e i processi non spontanei dell'anabolismo. Nei termini della termodinamica del non equilibrio, il metabolismo mantiene l'ordine, creando disordine.[97]
Regolazione e controllo
[modifica | modifica wikitesto]Poiché gli ambienti dove vive la maggior parte degli organismi sono in costante evoluzione, le reazioni metaboliche devono essere finemente regolate per mantenere una serie costante di condizioni all'interno delle cellule, chiamata omeostasi.[98][99] La regolazione metabolica consente anche agli organismi di rispondere ai segnali e a interagire attivamente con i loro ambienti.[100] Due concetti strettamente legati sono importanti per capire come le vie metaboliche vengono controllate. In primo luogo, un enzima regola una via aumentando o diminuendo la sua attività in risposta a segnali. In secondo luogo, il controllo esercitato da questo enzima è dato dagli effetti che questi cambiamenti hanno sulla via su cui interagisce.[101] Per esempio un enzima può mostrare grandi variazioni di attività, ma se questi cambiamenti hanno uno scarso effetto sul flusso di una via metabolica, allora questo enzima non è coinvolto nel controllo del percorso.[102]

Vi sono più livelli di regolazione del metabolismo. Nel regolamento intrinseco la via metabolica si auto-regola per rispondere ai cambiamenti dei livelli dei substrati o dei prodotti; per esempio, una diminuzione della quantità di un prodotto può aumentare la via metabolica per compensarlo.[103] Questo tipo di regolazione comporta spesso una regolazione allosterica delle attività di più enzimi della via.[104] Il controllo estrinseco comporta che una cellula di un organismo multicellulare cambi il suo metabolismo in risposta a segnali provenienti da altre cellule. Generalmente questi segnali sono in forma di messaggeri solubili, come ormoni e fattori di crescita, e vengono rilevati da specifici recettori presenti sulla superficie delle cellule.[101] Questi segnali vengono quindi trasmessi all'interno della cellula da un secondo messaggero che spesso coinvolge la fosforilazione delle proteine.[105]
Un esempio molto ben studiato di un controllo estrinseco è la regolazione del metabolismo del glucosio da parte dell'ormone insulina.[106] L'insulina viene prodotta in risposta agli aumenti dei livelli di glucosio nel sangue. Il legame dell'ormone ai recettori dedicati sulle cellule comporta una cascata di protein-chinasi che porta le cellule ad assumere glucosio e convertirlo in molecole di immagazzinamento come acidi grassi e glicogeno.[107] Il metabolismo del glicogeno è controllato dall'attività di fosforilasi, l'enzima che scompone il glicogeno e la glicogeno(amido) sintasi, l'enzima che rende possibile ciò. Questi enzimi sono regolati in maniera reciproca, con la fosforilazione che inibisce la glicogeno sintasi, ma attiva la fosforilasi. L'insulina provoca la sintesi di glicogeno attivando la proteina fosfatasi e producendo una diminuzione della fosforilazione di questi enzimi.[108]
Evoluzione
[modifica | modifica wikitesto]
Le principali vie del metabolismo sopra descritte, quali la glicolisi e il ciclo dell'acido citrico, sono presenti in tutti e tre i dominii viventi (batteri, archea ed eucarioti) ed erano presenti nell'ultimo antenato comune universale.[3][109] Questa cellula ancestrale universale fu un procariote e probabilmente un metanogeno con un gran numero di aminoacidi, nucleotidi, carboidrati e con capacità di metabolismo dei lipidi.[110][111] La conservazione di queste antiche vie metaboliche durante l'evoluzione successiva potrebbe essere il risultato di queste reazioni, essendo stata una soluzione ottimale per i loro particolari problemi metabolici; infatti percorsi come la glicolisi e il ciclo dell'acido citrico sono in grado di produrre prodotti finali altamente efficienti e con un numero minimo di passaggi.[4][5] Mutazioni che interessano segmenti non codificanti di DNA comportano solo il cambiamento dell'efficienza metabolica dell'individuo per il quale si verifica tale mutazione.[112] Le prime vie metaboliche a base di enzimi, possono aver fatto parte del metabolismo delle purine, mentre precedenti percorsi metabolici potrebbero aver fatto parte dell'ipotesi del mondo a RNA.[113]
Molti modelli sono stati proposti per descrivere i meccanismi attraverso i quali le nuove vie metaboliche si siano evolute. Questi includono l'aggiunta sequenziale di nuovi enzimi in una via breve ancestrale, la duplicazione e divergenza di intere vie nonché l'assunzione di enzimi preesistenti e il loro assemblaggio in un percorso di reazione.[114] L'importanza relativa di questi meccanismi non è chiara, ma studi di genomica hanno dimostrato che gli enzimi in una via sono suscettibili di avere un antenato comune, il che suggerisce che molte vie si sono evolute in modo passo-passo con nuove funzioni create da fasi preesistenti della via metabolica.[115] Un modello alternativo viene dagli studi che ripercorrono l'evoluzione delle strutture proteiche in reti metaboliche, questo suggerisce che gli enzimi siano pervasivamente reclutati, prendendo a prestito gli enzimi per svolgere le funzioni simili in diverse vie metaboliche (evidenti nel database MANET).[116] Questo processo di assunzioni si traducono in un mosaico enzimatico evolutivo.[117] Una terza possibilità è che alcune parti del metabolismo potrebbero esistere come "moduli" che possono essere riutilizzati in diversi percorsi e svolgono funzioni analoghe su molecole diverse.[118]
Così come l'evoluzione può creare nuove vie metaboliche, l'evoluzione può anche causare la perdita di alcuni funzioni metaboliche. Per esempio, in alcuni parassiti i processi metabolici che non sono essenziali per la sopravvivenza si perdono e gli aminoacidi, i nucleotidi e i carboidrati possono invece essere eliminati dall'ospite.[119] Simili capacità di riduzione metabolica sono visti anche negli organismi endosimbiontici.[120]
Uno studio di John Speakman ha rilevato che il metabolismo, uguale a quello materno al momento della nascita, cresce fino al primo anno di vita per poi iniziare un rallentamento, si stabilizza dai 20 ai 60 anni e successivamente comincia il declino.[121]
Storia
[modifica | modifica wikitesto]
Il termine "metabolismo" deriva dalla parola greca Μεταβολισμός - "Metabolismos" che significa "cambiare" o "rovesciare".[122] I primi riferimenti al metabolismo documentati sono stati fatti, nel 1260 d.C., da Ibn al-Nafīs nel suo lavoro intitolato Al-Risalah al-Kamiliyyah fil Siera al-Nabawiyyah (Il Trattato di Kamil sulla biografia del Profeta), che includeva la seguente frase "Sia il corpo sia le sue parti sono in un continuo stato di dissoluzione e nutrimento, quindi subiscono inevitabilmente un cambiamento permanente".[123] La storia dello studio scientifico del metabolismo abbraccia diversi secoli ed è iniziata con l'esame di interi animali nei primi studi, fino ad arrivare alle singole reazioni metaboliche nella biochimica moderna. I primi esperimenti controllati sul metabolismo umano sono stati pubblicati da Santorio Santorio nel 1614 nel suo libro Ars de statica medicina.[124] Egli descrisse osservazioni sul suo stesso peso corporeo prima e dopo i pasti, dopo aver dormito, lavorato o avuto rapporti sessuali, dopo il digiuno o dopo aver bevuto o escreto. Egli scoprì che la maggior parte del cibo veniva perso attraverso quello che lui chiamava "traspirazione insensibile".
In questi primi studi i meccanismi di questi processi metabolici non erano stati identificati e si riteneva che vi fosse una forza vitale che animasse i tessuti viventi.[125] Nel XIX secolo, mentre studiava la fermentazione dello zucchero in alcool da lievito, Louis Pasteur concluse che la fermentazione fosse catalizzata da sostanze all'interno delle cellule di lievito, che definì "fermenti". Egli scrisse che "la fermentazione alcolica è un atto correlato con la vita e l'organizzazione delle cellule di lievito, non con la morte o la putrefazione delle cellule".[126] Questa scoperta, insieme alla pubblicazione di Friedrich Wöhler nel 1828 di un documento sulla sintesi chimica dell'urea,[127] si distingue per essere il primo composto organico preparato da precursori del tutto inorganici. Ciò dimostrò che i composti organici e le reazioni chimiche presenti nelle cellule non erano diverse in linea di principio di qualsiasi altra branca della chimica.
La scoperta degli enzimi, avvenuta all'inizio del XX secolo per opera di Eduard Buchner, separò lo studio delle reazioni chimiche del metabolismo dallo studio biologico delle cellule e segnò l'inizio della disciplina della biochimica.[128] La mole di conoscenze biochimiche crebbe rapidamente per tutto il secolo. Uno dei biochimici più prolifici di questi tempi fu Hans Adolf Krebs che fornì enormi contributi allo studio del metabolismo.[129] Egli scoprì e descrisse il ciclo dell'urea e, in seguito lavorando con Hans Kornberg, il ciclo dell'acido citrico e il ciclo del gliossilato.[130][65] La ricerca biochimica moderna ha beneficiato notevolmente dello sviluppo di nuove tecniche, come la cromatografia, la cristallografia a raggi X, la spettroscopia di risonanza magnetica nucleare, la marcatura radioisotopica, la microscopia elettronica e le simulazioni di dinamica molecolare. Queste tecniche hanno permesso la scoperta e l'analisi dettagliata delle numerose molecole e vie metaboliche delle cellule.
Prospettive terapeutiche
[modifica | modifica wikitesto]Al momento la terapia delle alterazioni metaboliche è affidata al recupero della patologia di base e solo di recente si sono avviate delle procedure, ancora sotto studio, che tengano sotto controllo una delle cause più frequenti delle alterazioni metaboliche, non secondarie a patologie primarie già accertate.
Effetti della musicoterapia sul metabolismo
[modifica | modifica wikitesto]Lo studio delle effettive capacità terapeutiche della musica (musicoterapia) è solo agli inizi. Studi recenti hanno dimostrato un ruolo della musica nel recupero metabolico dallo stress, nella motilità gastrica e intestinale, nella modulazione dei sintomi gastrointestinali legati al cancro, e nell'aumento del metabolismo lipidico e della clearance dell'acido lattico durante l'esercizio e il recupero dopo lo sforzo.[131] Diversi studi hanno dimostrato il ruolo della musica nella diminuzione del livello di cortisolo in relazione alle operazioni chirurgiche.[132]
In relazione all'atto chirurgico si assiste fisiologicamente a una risposta ipermetabolica caratterizzata dal rilascio di catecolamine, cortisolo, citochine e altri ormoni neuroendocrini modulati dall'asse ipotalamo-ipofisario e dal sistema nervoso autonomo. Questo intenso processo catabolico è facilitato in parte dall'ipercortisolemia attraverso la promozione di glicogenolisi, lipolisi e proteolisi. La musica abbassa il livello del cortisolo, attraverso questa azione è verosimile che intervenga nell'abbassare il metabolismo energetico il cui aumento è particolarmente dannoso, per esempio, nei bambini ustionati.[133]
Il primo passo per comprendere come la musica medi il rilassamento dallo stress è che essa aumenta i livelli di GH, attraverso il quale interviene direttamente sull'asse ipotalamo-ipofisario. L'ormone dell'accrescimento (GH) è un ormone anabolico che stimola lo smantellamento dei triacilgliceroli, sopprime l'assorbimento cellulare dei lipidi circolanti, media effetti stimolanti la crescita in un'ampia gamma di tessuti stimolando la secrezione del fattore di crescita insulino-simile-1. Nelle fasi iniziali di una lesione, come parte della risposta acuta allo stress, si manifesta una resistenza al GH. Diversi studi suggeriscono che la musica potrebbe moderare questo effetto. Ciò è stato osservato in pazienti in condizioni critiche nei quali è stato rilevato un aumento significativo della concentrazione di GH dopo l'esposizione a musica rilassante. Essi mostrarono anche una concomitante diminuzione di interleuchina-6 (citochina proinfiammatoria) e dell'adrenalina in conseguenza all'aumento dei livelli di GH.[134]
La risposta del sistema nervoso autonomo verosimilmente gioca un ruolo importante nel mediare gli effetti della musica sull'attività immunitaria e neuro-ormonale. La musica, infatti, ha la capacità di indurre un'attività mentale ed emozionale in grado di modulare il funzionamento del sistema nervoso autonomo.[135]
Gli studi che si sono occupati dell'impatto della musica sulle variabili cardiovascolari hanno trovato un aumento dei livelli di ormone rilasciante la corticotropina e di ormone adrenocorticotropo in pazienti con insufficienza cardiaca cronica, suggerendo la presenza di un feedback disfunzionale e un aumento dell'attività dell'asse ipotalamo-ipofisario nell'insufficienza cardiaca cronica.[136] La variabilità della frequenza cardiaca (HRV), insieme al livello sierico dell'adrenalina e della noradrenalina, è generalmente considerato il metodo standard per valutare quantitativamente l'attività cardiaca autonoma. Nei pazienti con insufficienza cardiaca cronica un alto HRV è correlato con una migliore prognosi, viceversa, una diminuzione dell'HRV è associata a una prognosi peggiore. In due diversi studi è emerso che la musicoterapia porta a un significativo aumento dei parametri dell'HRV suggerendo un'attivazione musica-indotta del parasimpatico. Parallelamente il tono simpatico si è dimostrato essere attenuato in pazienti sottoposti a musicoterapia in quanto i pazienti mostravano livelli significativamente inferiori di adrenalina e noradrenalina rispetto ai gruppi di controllo.[137]
Durante l'esercizio la musica viene comunemente utilizzata per bilanciare la fatica fisica ed emotiva e migliorare la performance. Recenti ricerche hanno portato evidenze fisiologiche sul ruolo della musica nel migliorare la performance, migliorando il profilo lipidico e facilitando il recupero post-esercizio. Uno dei primi lavori fatto su atleti della corsa ha dimostrato che l'ascolto di musica veloce aumentava i livelli di cortisolo ematico. Avendo il cortisolo un ruolo nel promuovere il catabolismo dei substrati energetici nei tessuti muscolare, adiposo e connettivo, ciò suggerisce un potenziale vantaggio metabolico nell'impiego della musica ad alto ritmo durante l'esercizio.[138]
La musica potrebbe anche avere un ruolo di rinforzo degli effetti dell'esercizio nel migliorare il profilo lipidico. In uno studio sulla resistenza al training in donne obese, i soggetti che ascoltavano la musica durante in training hanno mostrato un significativo aumento di lipoproteine ad alta densità e una significativa diminuzione del colesterolo totale, delle LDL e della percentuale totale di grasso corporeo, risultati non osservati nel gruppo di controllo.[139]
La musica può facilitare il recupero dopo esercizio intenso. In uno studio condotto su maschi allenati in età da college, l'ascolto di musica dopo sessioni di corsa intensa ha portato a una significativa diminuzione della concentrazione del lattato ematico, rispetto al controllo.[140]
Note
[modifica | modifica wikitesto]- ^ a b Friedrich C, Physiology and genetics of sulfur-oxidizing bacteria, in Adv Microb Physiol, Advances in Microbial Physiology, vol. 39, 1998, pp. 235-89, DOI:10.1016/S0065-2911(08)60018-1, ISBN 978-0-12-027739-1, PMID 9328649.
- ^ Pace NR, The universal nature of biochemistry, in Proc. Natl. Acad. Sci. U.S.A., vol. 98, n. 3, gennaio 2001, pp. 805-8, Bibcode:2001PNAS...98..805P, DOI:10.1073/pnas.98.3.805, PMC 33372, PMID 11158550.
- ^ a b Smith E, Morowitz H, Universality in intermediary metabolism, in Proc Natl Acad Sci USA, vol. 101, n. 36, 2004, pp. 13168-73, Bibcode:2004PNAS..10113168S, DOI:10.1073/pnas.0404922101, PMC 516543, PMID 15340153.
- ^ a b Ebenhöh O, Heinrich R, Evolutionary optimization of metabolic pathways. Theoretical reconstruction of the stoichiometry of ATP and NADH producing systems, in Bull Math Biol, vol. 63, n. 1, 2001, pp. 21-55, DOI:10.1006/bulm.2000.0197, PMID 11146883.
- ^ a b Meléndez-Hevia E, Waddell T, Cascante M, The puzzle of the Krebs citric acid cycle: assembling the pieces of chemically feasible reactions, and opportunism in the design of metabolic pathways during evolution, in J Mol Evol, vol. 43, n. 3, 1996, pp. 293-303, DOI:10.1007/BF02338838, PMID 8703096.
- ^ Michie K, Löwe J, Dynamic filaments of the bacterial cytoskeleton, in Annu Rev Biochem, vol. 75, 2006, pp. 467-92, DOI:10.1146/annurev.biochem.75.103004.142452, PMID 16756499.
- ^ a b c d e Nelson, p. 841.
- ^ Kelleher, J,Bryan 3rd, B, Mallet,R, Holleran, A, Murphy, A, and Fiskum, G, Analysis of tricarboxylic acid-cycle metabolism of hepatoma cells by comparison of 14CO2 ratios, in Biochem J, vol. 246, n. 3, 1987, pp. 633-639, PMC 346906, PMID 6752947.
- ^ Hothersall, J and Ahmed, A, Metabolic fate of the increased yeast amino acid uptake subsequent to catabolite derepression, in J Amino Acids, vol. 2013, 2013, pp. e461901, DOI:10.1155/2013/461901, PMC 3575661, PMID 23431419.
- ^ Fahy E, Subramaniam S, Brown H, Glass C, Merrill A, Murphy R, Raetz C, Russell D, Seyama Y, Shaw W, Shimizu T, Spener F, van Meer G, VanNieuwenhze M, White S, Witztum J, Dennis E, A comprehensive classification system for lipids, in J Lipid Res, vol. 46, n. 5, 2005, pp. 839-61, DOI:10.1194/jlr.E400004-JLR200, PMID 15722563. URL consultato il 20 agosto 2015 (archiviato dall'url originale il 24 agosto 2010).
- ^ Nomenclature of Lipids, su chem.qmul.ac.uk, IUPAC-IUB Commission on Biochemical Nomenclature (CBN). URL consultato l'8 marzo 2007.
- ^ Hegardt F, Mitochondrial 3-hydroxy-3-methylglutaryl-CoA synthase: a control enzyme in ketogenesis, in Biochem J, vol. 338, Pt 3, 1999, pp. 569-82, DOI:10.1042/0264-6021:3380569, PMC 1220089, PMID 10051425.
- ^ Raman R, Raguram S, Venkataraman G, Paulson J, Sasisekharan R, Glycomics: an integrated systems approach to structure-function relationships of glycans, in Nat Methods, vol. 2, n. 11, 2005, pp. 817-24, DOI:10.1038/nmeth807, PMID 16278650.
- ^ Sierra S, Kupfer B, Kaiser R, Basics of the virology of HIV-1 and its replication, in J Clin Virol, vol. 34, n. 4, 2005, pp. 233-44, DOI:10.1016/j.jcv.2005.09.004, PMID 16198625.
- ^ a b Wimmer M, Rose I, Mechanisms of enzyme-catalyzed group transfer reactions, in Annu Rev Biochem, vol. 47, 1978, pp. 1031-78, DOI:10.1146/annurev.bi.47.070178.005123, PMID 354490.
- ^ Mitchell P, The Ninth Sir Hans Krebs Lecture. Compartmentation and communication in living systems. Ligand conduction: a general catalytic principle in chemical, osmotic and chemiosmotic reaction systems, in Eur J Biochem, vol. 95, n. 1, 1979, pp. 1-20, DOI:10.1111/j.1432-1033.1979.tb12934.x, PMID 378655.
- ^ a b c d e Dimroth P, von Ballmoos C, Meier T, Catalytic and mechanical cycles in F-ATP synthases: Fourth in the Cycles Review Series, in EMBO Rep, vol. 7, n. 3, marzo 2006, pp. 276-82, DOI:10.1038/sj.embor.7400646, PMC 1456893, PMID 16607397.
- ^ Ann Coulston, John Kerner, JoAnn Hattner e Ashini Srivastava, Nutrition Principles and Clinical Nutrition, in Stanford School of Medicine Nutrition Courses, SUMMIT, 2006.
- ^ Pollak N, Dölle C, Ziegler M, The power to reduce: pyridine nucleotides – small molecules with a multitude of functions, in Biochem J, vol. 402, n. 2, 2007, pp. 205-18, DOI:10.1042/BJ20061638, PMC 1798440, PMID 17295611.
- ^ a b Heymsfield S, Waki M, Kehayias J, Lichtman S, Dilmanian F, Kamen Y, Wang J, Pierson R, Chemical and elemental analysis of humans in vivo using improved body composition models, in Am J Physiol, vol. 261, 2 Pt 1, 1991, pp. E190–8, PMID 1872381.
- ^ Sychrová H, Yeast as a model organism to study transport and homeostasis of alkali metal cations (PDF), in Physiol Res, 53 Suppl 1, 2004, pp. S91–8, PMID 15119939.
- ^ Levitan I, Modulation of ion channels in neurons and other cells, in Annu Rev Neurosci, vol. 11, 1988, pp. 119-36, DOI:10.1146/annurev.ne.11.030188.001003, PMID 2452594.
- ^ Dulhunty A, Excitation-contraction coupling from the 1950s into the new millennium, in Clin Exp Pharmacol Physiol, vol. 33, n. 9, 2006, pp. 763-72, DOI:10.1111/j.1440-1681.2006.04441.x, PMID 16922804.
- ^ Mahan D, Shields R, Macro- and micromineral composition of pigs from birth to 145 kilograms of body weight, in J Anim Sci, vol. 76, n. 2, 1998, pp. 506-12, PMID 9498359 (archiviato dall'url originale il 30 aprile 2011).
- ^ Husted S, Mikkelsen B, Jensen J, Nielsen N, Elemental fingerprint analysis of barley (Hordeum vulgare) using inductively coupled plasma mass spectrometry, isotope-ratio mass spectrometry, and multivariate statistics, in Anal Bioanal Chem, vol. 378, n. 1, 2004, pp. 171-82, DOI:10.1007/s00216-003-2219-0, PMID 14551660.
- ^ Finney L, O'Halloran T, Transition metal speciation in the cell: insights from the chemistry of metal ion receptors, in Science, vol. 300, n. 5621, 2003, pp. 931-6, Bibcode:2003Sci...300..931F, DOI:10.1126/science.1085049, PMID 12738850.
- ^ Cousins R, Liuzzi J, Lichten L, Mammalian zinc transport, trafficking, and signals, in J Biol Chem, vol. 281, n. 34, 2006, pp. 24085-9, DOI:10.1074/jbc.R600011200, PMID 16793761. URL consultato il 20 agosto 2015 (archiviato dall'url originale il 5 novembre 2008).
- ^ Dunn L, Rahmanto Y, Richardson D, Iron uptake and metabolism in the new millennium, in Trends Cell Biol, vol. 17, n. 2, 2007, pp. 93-100, DOI:10.1016/j.tcb.2006.12.003, PMID 17194590.
- ^ Nealson K, Conrad P, Life: past, present and future, in Philos Trans R Soc Lond B Biol Sci, vol. 354, n. 1392, 1999, pp. 1923-39, DOI:10.1098/rstb.1999.0532, PMC 1692713, PMID 10670014.
- ^ Nelson N, Ben-Shem A, The complex architecture of oxygenic photosynthesis, in Nat Rev Mol Cell Biol, vol. 5, n. 12, 2004, pp. 971-82, DOI:10.1038/nrm1525, PMID 15573135.
- ^ Häse C, Finkelstein R, Bacterial extracellular zinc-containing metalloproteases, in Microbiol Rev, vol. 57, n. 4, dicembre 1993, pp. 823-37, PMC 372940, PMID 8302217.
- ^ Gupta R, Gupta N, Rathi P, Bacterial lipases: an overview of production, purification and biochemical properties, in Appl Microbiol Biotechnol, vol. 64, n. 6, 2004, pp. 763-81, DOI:10.1007/s00253-004-1568-8, PMID 14966663.
- ^ Hoyle T, The digestive system: linking theory and practice, in Br J Nurs, vol. 6, n. 22, 1997, pp. 1285-91, PMID 9470654.
- ^ Souba W, Pacitti A, How amino acids get into cells: mechanisms, models, menus, and mediators, in JPEN J Parenter Enteral Nutr, vol. 16, n. 6, 1992, pp. 569-78, DOI:10.1177/0148607192016006569, PMID 1494216.
- ^ Barrett M, Walmsley A, Gould G, Structure and function of facilitative sugar transporters, in Curr Opin Cell Biol, vol. 11, n. 4, 1999, pp. 496-502, DOI:10.1016/S0955-0674(99)80072-6, PMID 10449337.
- ^ Bell G, Burant C, Takeda J, Gould G, Structure and function of mammalian facilitative sugar transporters, in J Biol Chem, vol. 268, n. 26, 1993, pp. 19161-4, PMID 8366068.
- ^ a b Bouché C, Serdy S, Kahn C, Goldfine A, The cellular fate of glucose and its relevance in type 2 diabetes, in Endocr Rev, vol. 25, n. 5, 2004, pp. 807-30, DOI:10.1210/er.2003-0026, PMID 15466941. URL consultato il 27 agosto 2015 (archiviato dall'url originale il 4 dicembre 2012).
- ^ Matthew, F. Wipperman, Suzanne, T. Thomas e Nicole, S. Sampson, Pathogen roid rage: Cholesterol utilization by Mycobacterium tuberculosis, in Crit. Rev. Biochem. Mol. Biol., vol. 49, n. 4, 2014, pp. 269-93, DOI:10.3109/10409238.2014.895700, PMID 24611808.
- ^ Sakami W, Harrington H, Amino acid metabolism, in Annu Rev Biochem, vol. 32, 1963, pp. 355-98, DOI:10.1146/annurev.bi.32.070163.002035, PMID 14144484.
- ^ Brosnan J, Glutamate, at the interface between amino acid and carbohydrate metabolism, in J Nutr, vol. 130, 4S Suppl, 2000, pp. 988S–90S, PMID 10736367.
- ^ Young V, Ajami A, Glutamine: the emperor or his clothes?, in J Nutr, vol. 131, 9 Suppl, 2001, pp. 2449S–59S; discussion 2486S–7S, PMID 11533293.
- ^ Hosler J, Ferguson-Miller S, Mills D, Energy Transduction: Proton Transfer Through the Respiratory Complexes, in Annu Rev Biochem, vol. 75, 2006, pp. 165-87, DOI:10.1146/annurev.biochem.75.062003.101730, PMC 2659341, PMID 16756489.
- ^ Schultz B, Chan S, Structures and proton-pumping strategies of mitochondrial respiratory enzymes, in Annu Rev Biophys Biomol Struct, vol. 30, 2001, pp. 23-65, DOI:10.1146/annurev.biophys.30.1.23, PMID 11340051.
- ^ Capaldi R, Aggeler R, Mechanism of the F(1)F(0)-type ATP synthase, a biological rotary motor, in Trends Biochem Sci, vol. 27, n. 3, 2002, pp. 154-60, DOI:10.1016/S0968-0004(01)02051-5, PMID 11893513.
- ^ Friedrich B, Schwartz E, Molecular biology of hydrogen utilization in aerobic chemolithotrophs, in Annu Rev Microbiol, vol. 47, 1993, pp. 351-83, DOI:10.1146/annurev.mi.47.100193.002031, PMID 8257102.
- ^ Weber K, Achenbach L, Coates J, Microorganisms pumping iron: anaerobic microbial iron oxidation and reduction, in Nat Rev Microbiol, vol. 4, n. 10, 2006, pp. 752-64, DOI:10.1038/nrmicro1490, PMID 16980937.
- ^ Jetten M, Strous M, van de Pas-Schoonen K, Schalk J, van Dongen U, van de Graaf A, Logemann S, Muyzer G, van Loosdrecht M, Kuenen J, The anaerobic oxidation of ammonium, in FEMS Microbiol Rev, vol. 22, n. 5, 1998, pp. 421-37, DOI:10.1111/j.1574-6976.1998.tb00379.x, PMID 9990725.
- ^ Simon J, Enzymology and bioenergetics of respiratory nitrite ammonification, in FEMS Microbiol Rev, vol. 26, n. 3, 2002, pp. 285-309, DOI:10.1111/j.1574-6976.2002.tb00616.x, PMID 12165429.
- ^ Conrad R, Soil microorganisms as controllers of atmospheric trace gases (H2, CO, CH4, OCS, N2O, and NO), in Microbiol Rev, vol. 60, n. 4, 1996, pp. 609-40, PMC 239458, PMID 8987358.
- ^ Barea J, Pozo M, Azcón R, Azcón-Aguilar C, Microbial co-operation in the rhizosphere, in J Exp Bot, vol. 56, n. 417, 2005, pp. 1761-78, DOI:10.1093/jxb/eri197, PMID 15911555.
- ^ van der Meer M, Schouten S, Bateson M, Nübel U, Wieland A, Kühl M, de Leeuw J, Sinninghe Damsté J, Ward D, Diel Variations in Carbon Metabolism by Green Nonsulfur-Like Bacteria in Alkaline Siliceous Hot Spring Microbial Mats from Yellowstone National Park, in Appl Environ Microbiol, vol. 71, n. 7, luglio 2005, pp. 3978-86, DOI:10.1128/AEM.71.7.3978-3986.2005, PMC 1168979, PMID 16000812.
- ^ Tichi M, Tabita F, Interactive Control of Rhodobacter capsulatus Redox-Balancing Systems during Phototrophic Metabolism, in J Bacteriol, vol. 183, n. 21, 2001, pp. 6344-54, DOI:10.1128/JB.183.21.6344-6354.2001, PMC 100130, PMID 11591679.
- ^ Allen J, Williams J, Photosynthetic reaction centers, in FEBS Lett, vol. 438, 1–2, 1998, pp. 5-9, DOI:10.1016/S0014-5793(98)01245-9, PMID 9821949.
- ^ Munekage Y, Hashimoto M, Miyake C, Tomizawa K, Endo T, Tasaka M, Shikanai T, Cyclic electron flow around photosystem I is essential for photosynthesis, in Nature, vol. 429, n. 6991, 2004, pp. 579-82, Bibcode:2004Natur.429..579M, DOI:10.1038/nature02598, PMID 15175756.
- ^ Miziorko H, Lorimer G, Ribulose-1,5-bisphosphate carboxylase-oxygenase, in Annu Rev Biochem, vol. 52, 1983, pp. 507-35, DOI:10.1146/annurev.bi.52.070183.002451, PMID 6351728.
- ^ Dodd A, Borland A, Haslam R, Griffiths H, Maxwell K, Crassulacean acid metabolism: plastic, fantastic, in J Exp Bot, vol. 53, n. 369, 2002, pp. 569-80, DOI:10.1093/jexbot/53.369.569, PMID 11886877.
- ^ Hügler M, Wirsen C, Fuchs G, Taylor C, Sievert S, Evidence for Autotrophic CO2 Fixation via the Reductive Tricarboxylic Acid Cycle by Members of the ɛ Subdivision of Proteobacteria, in J Bacteriol, vol. 187, n. 9, maggio 2005, pp. 3020-7, DOI:10.1128/JB.187.9.3020-3027.2005, PMC 1082812, PMID 15838028.
- ^ Strauss G, Fuchs G, Enzymes of a novel autotrophic CO2 fixation pathway in the phototrophic bacterium Chloroflexus aurantiacus, the 3-hydroxypropionate cycle, in Eur J Biochem, vol. 215, n. 3, 1993, pp. 633-43, DOI:10.1111/j.1432-1033.1993.tb18074.x, PMID 8354269.
- ^ Wood H, Life with CO or CO2 and H2 as a source of carbon and energy, in FASEB J, vol. 5, n. 2, 1991, pp. 156-63, PMID 1900793.
- ^ Shively J, van Keulen G, Meijer W, Something from almost nothing: carbon dioxide fixation in chemoautotrophs, in Annu Rev Microbiol, vol. 52, 1998, pp. 191-230, DOI:10.1146/annurev.micro.52.1.191, PMID 9891798.
- ^ Boiteux A, Hess B, Design of glycolysis, in Philos Trans R Soc Lond B Biol Sci, vol. 293, n. 1063, 1981, pp. 5-22, Bibcode:1981RSPTB.293....5B, DOI:10.1098/rstb.1981.0056, PMID 6115423.
- ^ Pilkis S, el-Maghrabi M, Claus T, Fructose-2,6-bisphosphate in control of hepatic gluconeogenesis. From metabolites to molecular genetics, in Diabetes Care, vol. 13, n. 6, 1990, pp. 582-99, DOI:10.2337/diacare.13.6.582, PMID 2162755.
- ^ a b Ensign S, Revisiting the glyoxylate cycle: alternate pathways for microbial acetate assimilation, in Mol Microbiol, vol. 61, n. 2, 2006, pp. 274-6, DOI:10.1111/j.1365-2958.2006.05247.x, PMID 16856935.
- ^ Finn P, Dice J, Proteolytic and lipolytic responses to starvation, in Nutrition, vol. 22, 7–8, 2006, pp. 830-44, DOI:10.1016/j.nut.2006.04.008, PMID 16815497.
- ^ a b Kornberg H, Krebs H, Synthesis of cell constituents from C2-units by a modified tricarboxylic acid cycle, in Nature, vol. 179, n. 4568, 1957, pp. 988-91, DOI:10.1038/179988a0, PMID 13430766.
- ^ Rademacher T, Parekh R, Dwek R, Glycobiology, in Annu Rev Biochem, vol. 57, 1988, pp. 785-838, DOI:10.1146/annurev.bi.57.070188.004033, PMID 3052290.
- ^ Opdenakker G, Rudd P, Ponting C, Dwek R, Concepts and principles of glycobiology, in FASEB J, vol. 7, n. 14, 1993, pp. 1330-7, PMID 8224606.
- ^ McConville M, Menon A, Recent developments in the cell biology and biochemistry of glycosylphosphatidylinositol lipids (review), in Mol Membr Biol, vol. 17, n. 1, 2000, pp. 1-16, DOI:10.1080/096876800294443, PMID 10824734.
- ^ Chirala S, Wakil S, Structure and function of animal fatty acid synthase, in Lipids, vol. 39, n. 11, 2004, pp. 1045-53, DOI:10.1007/s11745-004-1329-9, PMID 15726818.
- ^ White S, Zheng J, Zhang Y, The structural biology of type II fatty acid biosynthesis, in Annu Rev Biochem, vol. 74, 2005, pp. 791-831, DOI:10.1146/annurev.biochem.74.082803.133524, PMID 15952903.
- ^ Ohlrogge J, Jaworski J, Regulation of fatty acid synthesis, in Annu Rev Plant Physiol Plant Mol Biol, vol. 48, 1997, pp. 109-136, DOI:10.1146/annurev.arplant.48.1.109, PMID 15012259.
- ^ Dubey V, Bhalla R, Luthra R, An overview of the non-mevalonate pathway for terpenoid biosynthesis in plants (PDF), in J Biosci, vol. 28, n. 5, 2003, pp. 637-46, DOI:10.1007/BF02703339, PMID 14517367.
- ^ a b Kuzuyama T, Seto H, Diversity of the biosynthesis of the isoprene units, in Nat Prod Rep, vol. 20, n. 2, 2003, pp. 171-83, DOI:10.1039/b109860h, PMID 12735695.
- ^ Grochowski L, Xu H, White R, Methanocaldococcus jannaschii Uses a Modified Mevalonate Pathway for Biosynthesis of Isopentenyl Diphosphate, in J Bacteriol, vol. 188, n. 9, maggio 2006, pp. 3192-8, DOI:10.1128/JB.188.9.3192-3198.2006, PMC 1447442, PMID 16621811.
- ^ Lichtenthaler H, The 1-Ddeoxy-D-xylulose-5-phosphate pathway of isoprenoid biosynthesis in plants, in Annu Rev Plant Physiol Plant Mol Biol, vol. 50, 1999, pp. 47-65, DOI:10.1146/annurev.arplant.50.1.47, PMID 15012203.
- ^ a b Schroepfer G, Sterol biosynthesis, in Annu Rev Biochem, vol. 50, 1981, pp. 585-621, DOI:10.1146/annurev.bi.50.070181.003101, PMID 7023367.
- ^ Lees N, Skaggs B, Kirsch D, Bard M, Cloning of the late genes in the ergosterol biosynthetic pathway of Saccharomyces cerevisiae—a review, in Lipids, vol. 30, n. 3, 1995, pp. 221-6, DOI:10.1007/BF02537824, PMID 7791529.
- ^ Himmelreich R, Hilbert H, Plagens H, Pirkl E, Li BC, Herrmann R, Complete sequence analysis of the genome of the bacterium Mycoplasma pneumoniae, in Nucleic Acids Res., vol. 24, n. 22, novembre 1996, pp. 4420-49, DOI:10.1093/nar/24.22.4420, PMC 146264, PMID 8948633.
- ^ Arthur C. Guyton e John E. Hall, Textbook of Medical Physiology, Philadelphia, Elsevier, 2006, pp. 855–6, ISBN 0-7216-0240-1.
- ^ Ibba M, Söll D, The renaissance of aminoacyl-tRNA synthesis, in EMBO Rep, vol. 2, n. 5, 2001, pp. 382–7, DOI:10.1093/embo-reports/kve095, PMC 1083889, PMID 11375928 (archiviato dall'url originale il 1º maggio 2011).
- ^ Lengyel P, Söll D, Mechanism of protein biosynthesis, in Bacteriol Rev, vol. 33, n. 2, 1969, pp. 264-301, PMC 378322, PMID 4896351.
- ^ a b Rudolph F, The biochemistry and physiology of nucleotides, in J Nutr, vol. 124, 1 Suppl, 1994, pp. 124S–127S, PMID 8283301. Zrenner R, Stitt M, Sonnewald U, Boldt R, Pyrimidine and purine biosynthesis and degradation in plants, in Annu Rev Plant Biol, vol. 57, 2006, pp. 805-36, DOI:10.1146/annurev.arplant.57.032905.105421, PMID 16669783.
- ^ Stasolla C, Katahira R, Thorpe T, Ashihara H, Purine and pyrimidine nucleotide metabolism in higher plants, in J Plant Physiol, vol. 160, n. 11, 2003, pp. 1271-95, DOI:10.1078/0176-1617-01169, PMID 14658380.
- ^ Davies O, Mendes P, Smallbone K, Malys N, Characterisation of multiple substrate-specific (d)ITP/(d)XTPase and modelling of deaminated purine nucleotide metabolism, in BMB Reports, vol. 45, n. 4, 2012, pp. 259-64, DOI:10.5483/BMBRep.2012.45.4.259, PMID 22531138.
- ^ Smith J, Enzymes of nucleotide synthesis, in Curr Opin Struct Biol, vol. 5, n. 6, 1995, pp. 752-7, DOI:10.1016/0959-440X(95)80007-7, PMID 8749362.
- ^ Testa B, Krämer S, The biochemistry of drug metabolism—an introduction: part 1. Principles and overview, in Chem Biodivers, vol. 3, n. 10, 2006, pp. 1053-101, DOI:10.1002/cbdv.200690111, PMID 17193224.
- ^ Danielson P, The cytochrome P450 superfamily: biochemistry, evolution and drug metabolism in humans, in Curr Drug Metab, vol. 3, n. 6, 2002, pp. 561-97, DOI:10.2174/1389200023337054, PMID 12369887.
- ^ King C, Rios G, Green M, Tephly T, UDP-glucuronosyltransferases, in Curr Drug Metab, vol. 1, n. 2, 2000, pp. 143-61, DOI:10.2174/1389200003339171, PMID 11465080.
- ^ Sheehan D, Meade G, Foley V, Dowd C, Structure, function and evolution of glutathione transferases: implications for classification of non-mammalian members of an ancient enzyme superfamily, in Biochem J, vol. 360, Pt 1, novembre 2001, pp. 1-16, DOI:10.1042/0264-6021:3600001, PMC 1222196, PMID 11695986.
- ^ Galvão T, Mohn W, de Lorenzo V, Exploring the microbial biodegradation and biotransformation gene pool, in Trends Biotechnol, vol. 23, n. 10, 2005, pp. 497-506, DOI:10.1016/j.tibtech.2005.08.002, PMID 16125262.
- ^ Janssen D, Dinkla I, Poelarends G, Terpstra P, Bacterial degradation of xenobiotic compounds: evolution and distribution of novel enzyme activities, in Environ Microbiol, vol. 7, n. 12, 2005, pp. 1868-82, DOI:10.1111/j.1462-2920.2005.00966.x, PMID 16309386.
- ^ Davies K, Oxidative stress: the paradox of aerobic life, in Biochem Soc Symp, vol. 61, 1995, pp. 1-31, PMID 8660387.
- ^ Tu B, Weissman J, Oxidative protein folding in eukaryotes: mechanisms and consequences, in J Cell Biol, vol. 164, n. 3, 2004, pp. 341-6, DOI:10.1083/jcb.200311055, PMC 2172237, PMID 14757749.
- ^ Sies H, Oxidative stress: oxidants and antioxidants (PDF), in Exp Physiol, vol. 82, n. 2, 1997, pp. 291-5, DOI:10.1113/expphysiol.1997.sp004024, PMID 9129943. URL consultato il 5 settembre 2015 (archiviato dall'url originale il 25 marzo 2009).
- ^ Vertuani S, Angusti A, Manfredini S, The antioxidants and pro-antioxidants network: an overview, in Curr Pharm Des, vol. 10, n. 14, 2004, pp. 1677-94, DOI:10.2174/1381612043384655, PMID 15134565.
- ^ von Stockar U, Liu J, Does microbial life always feed on negative entropy? Thermodynamic analysis of microbial growth, in Biochim Biophys Acta, vol. 1412, n. 3, 1999, pp. 191-211, DOI:10.1016/S0005-2728(99)00065-1, PMID 10482783.
- ^ Demirel Y, Sandler S, Thermodynamics and bioenergetics, in Biophys Chem, vol. 97, 2–3, 2002, pp. 87-111, DOI:10.1016/S0301-4622(02)00069-8, PMID 12050002.
- ^ Albert R, Scale-free networks in cell biology, in J Cell Sci, vol. 118, Pt 21, 2005, pp. 4947-57, DOI:10.1242/jcs.02714, PMID 16254242.
- ^ Brand M, Regulation analysis of energy metabolism, in J Exp Biol, vol. 200, Pt 2, 1997, pp. 193-202, PMID 9050227.
- ^ Soyer O, Salathé M, Bonhoeffer S, Signal transduction networks: topology, response and biochemical processes, in J Theor Biol, vol. 238, n. 2, 2006, pp. 416-25, DOI:10.1016/j.jtbi.2005.05.030, PMID 16045939.
- ^ a b Salter M, Knowles R, Pogson C, Metabolic control, in Essays Biochem, vol. 28, 1994, pp. 1-12, PMID 7925313.
- ^ Westerhoff H, Groen A, Wanders R, Modern theories of metabolic control and their applications (review), in Biosci Rep, vol. 4, n. 1, 1984, pp. 1-22, DOI:10.1007/BF01120819, PMID 6365197.
- ^ Fell D, Thomas S, Physiological control of metabolic flux: the requirement for multisite modulation, in Biochem J, vol. 311, Pt 1, 1995, pp. 35-9, PMC 1136115, PMID 7575476.
- ^ Hendrickson W, Transduction of biochemical signals across cell membranes, in Q Rev Biophys, vol. 38, n. 4, 2005, pp. 321-30, DOI:10.1017/S0033583506004136, PMID 16600054.
- ^ Cohen P, The regulation of protein function by multisite phosphorylation—a 25 year update, in Trends Biochem Sci, vol. 25, n. 12, 2000, pp. 596-601, DOI:10.1016/S0968-0004(00)01712-6, PMID 11116185.
- ^ Lienhard G, Slot J, James D, Mueckler M, How cells absorb glucose, in Sci Am, vol. 266, n. 1, 1992, pp. 86-91, DOI:10.1038/scientificamerican0192-86, PMID 1734513.
- ^ Roach P, Glycogen and its metabolism, in Curr Mol Med, vol. 2, n. 2, 2002, pp. 101-20, DOI:10.2174/1566524024605761, PMID 11949930.
- ^ Newgard C, Brady M, O'Doherty R, Saltiel A, Organizing glucose disposal: emerging roles of the glycogen targeting subunits of protein phosphatase-1 (PDF), in Diabetes, vol. 49, n. 12, 2000, pp. 1967-77, DOI:10.2337/diabetes.49.12.1967, PMID 11117996.
- ^ Romano A, Conway T, Evolution of carbohydrate metabolic pathways, in Res Microbiol, vol. 147, 6–7, 1996, pp. 448-55, DOI:10.1016/0923-2508(96)83998-2, PMID 9084754.
- ^ Koch A, How did bacteria come to be?, in Adv Microb Physiol, Advances in Microbial Physiology, vol. 40, 1998, pp. 353-99, DOI:10.1016/S0065-2911(08)60135-6, ISBN 978-0-12-027740-7, PMID 9889982.
- ^ Ouzounis C, Kyrpides N, The emergence of major cellular processes in evolution, in FEBS Lett, vol. 390, n. 2, 1996, pp. 119-23, DOI:10.1016/0014-5793(96)00631-X, PMID 8706840.
- ^ C.Michael Hogan. 2010. Mutation. ed. E.Monosson and C.J.Cleveland. Encyclopedia of Earth. National Council for Science and the Environment. Washington DC
- ^ Caetano-Anolles G, Kim HS, Mittenthal JE, The origin of modern metabolic networks inferred from phylogenomic analysis of protein architecture, in Proc Natl Acad Sci USA, vol. 104, n. 22, 2007, pp. 9358-63, Bibcode:2007PNAS..104.9358C, DOI:10.1073/pnas.0701214104, PMC 1890499, PMID 17517598.
- ^ Schmidt S, Sunyaev S, Bork P, Dandekar T, Metabolites: a helping hand for pathway evolution?, in Trends Biochem Sci, vol. 28, n. 6, 2003, pp. 336-41, DOI:10.1016/S0968-0004(03)00114-2, PMID 12826406.
- ^ Light S, Kraulis P, Network analysis of metabolic enzyme evolution in Escherichia coli, in BMC Bioinformatics, vol. 5, 2004, p. 15, DOI:10.1186/1471-2105-5-15, PMC 394313, PMID 15113413. Alves R, Chaleil R, Sternberg M, Evolution of enzymes in metabolism: a network perspective, in J Mol Biol, vol. 320, n. 4, 2002, pp. 751-70, DOI:10.1016/S0022-2836(02)00546-6, PMID 12095253.
- ^ Kim HS, Mittenthal JE, Caetano-Anolles G, MANET: tracing evolution of protein architecture in metabolic networks, in BMC Bioinformatics, vol. 7, 2006, p. 351, DOI:10.1186/1471-2105-7-351, PMC 1559654, PMID 16854231.
- ^ Teichmann SA, Rison SC, Thornton JM, Riley M, Gough J, Chothia C, Small-molecule metabolsim: an enzyme mosaic, in Trends Biotechnol, vol. 19, n. 12, 2001, pp. 482-6, DOI:10.1016/S0167-7799(01)01813-3, PMID 11711174.
- ^ Spirin V, Gelfand M, Mironov A, Mirny L, A metabolic network in the evolutionary context: Multiscale structure and modularity, in Proc Natl Acad Sci USA, vol. 103, n. 23, giugno 2006, pp. 8774-9, Bibcode:2006PNAS..103.8774S, DOI:10.1073/pnas.0510258103, PMC 1482654, PMID 16731630.
- ^ Lawrence J, Common themes in the genome strategies of pathogens, in Curr Opin Genet Dev, vol. 15, n. 6, 2005, pp. 584-8, DOI:10.1016/j.gde.2005.09.007, PMID 16188434. Wernegreen J, For better or worse: genomic consequences of intracellular mutualism and parasitism, in Curr Opin Genet Dev, vol. 15, n. 6, 2005, pp. 572-83, DOI:10.1016/j.gde.2005.09.013, PMID 16230003.
- ^ Pál C, Papp B, Lercher M, Csermely P, Oliver S, Hurst L, Chance and necessity in the evolution of minimal metabolic networks, in Nature, vol. 440, n. 7084, 2006, pp. 667-70, Bibcode:2006Natur.440..667P, DOI:10.1038/nature04568, PMID 16572170.
- ^ Il metabolismo cala solo dopo i 60 anni, stabile negli adulti, su ansa.it. URL consultato il 19 settembre 2023.
- ^ Metabolism, su etymonline.com, The Online Etymology Dictionary. URL consultato il 20 febbraio 2007.
- ^ Dr. Abu Shadi Al-Roubi (1982), "Ibn Al-Nafis as a philosopher", Symposium on Ibn al-Nafis, Second International Conference on Islamic Medicine: Islamic Medical Organization, Kuwait (cf. Ibn al-Nafis As a Philosopher, Encyclopedia of Islamic World)
- ^ Eknoyan G, Santorio Sanctorius (1561–1636) – founding father of metabolic balance studies, in Am J Nephrol, vol. 19, n. 2, 1999, pp. 226-33, DOI:10.1159/000013455, PMID 10213823.
- ^ (EN) Williams, H. S., A History of Science: in Five Volumes. Volume IV: Modern Development of the Chemical and Biological Sciences, su etext.lib.virginia.edu, Harper and Brothers (New York), 1904. URL consultato il 26 marzo 2007.
- ^ Dubos J., Louis Pasteur: Free Lance of Science, Gollancz. Quoted in Manchester K. L. (1995) Louis Pasteur (1822–1895)—chance and the prepared mind, in Trends Biotechnol, vol. 13, n. 12, 1951, pp. 511-515, DOI:10.1016/S0167-7799(00)89014-9, PMID 8595136.
- ^ Kinne-Saffran E, Kinne R, Vitalism and synthesis of urea. From Friedrich Wöhler to Hans A. Krebs, in Am J Nephrol, vol. 19, n. 2, 1999, pp. 290-4, DOI:10.1159/000013463, PMID 10213830.
- ^ (EN) Eduard Buchner's 1907, Nobel lecture, su nobelprize.org, https://www.nobelprize.org/. URL consultato il 20 marzo 2007.
- ^ Kornberg H, Krebs and his trinity of cycles, in Nat Rev Mol Cell Biol, vol. 1, n. 3, 2000, pp. 225-8, DOI:10.1038/35043073, PMID 11252898.
- ^ Krebs HA, Henseleit K, Untersuchungen über die Harnstoffbildung im tierkorper, in Z. Physiol. Chem., vol. 210, 1932, pp. 33-66, DOI:10.1515/bchm2.1932.210.1-2.33.
Krebs H, Johnson W, Metabolism of ketonic acids in animal tissues, in Biochem J, vol. 31, n. 4, aprile 1937, pp. 645-60, PMC 1266984, PMID 16746382. - ^ Alisa Yamasaki, B.A. et al., The impact of music on metabolism, su nutritionjrnl.com. URL consultato il 16 luglio 2016.
- ^ Leardi S et al., Randomized clinical trial examining the effect of music therapy in stress response to day surgery, in Br J Surg, n. 94, 2007, pp. 943-7. URL consultato il 16 luglio 2016.
- ^ Brillon DJ, Zheng B, Campbell RG, Matthews DE, Effect of cortisolo.
- ^ Conrad C et al., Overture for growth hormone: requiem for IL-6?, in Crit Care Med, n. 35, 2007, pp. 2709-13.
- ^ McCraty R et al., The effects of music on mood, tension, and mental clarity., in Altern Ther Health Med, n. 4, 1998, pp. 75-84.
- ^ Sivukhina EV et al., Altered hypothalamic–pituitary–adrenal axis activity in patients with chronic heart failure., in Horm Metab Res, n. 41, 2009, pp. 778-84.
- ^ Task Force of the European Society of Cardiology and North American Society of Pacing Electrophysiology., Heart rate variability: standards of measurement, physiological interpretation, and clinical use., in Circulation, n. 93, 1996, pp. 1043-65.
- ^ Brownley KA, McMurray RG, Hackney AC., Effects of music on physiological and affective responses to graded treadmill exercise in trained and untrained runners., in Int J Psychophysiol, n. 19, 1995, pp. 193-201.
- ^ Costa RR, Lima Alberton C, Tagliari M, Martins Kruel LF., Effects of resistance training on the lipid profile in obese women., in J Sports Med Phys Fitness, n. 51, 2011, pp. 169-77.
- ^ Eliakim M, Bodner E, Eliakim A, Nemet D, Meckel Y., Effect of motivational music on lactate levels during recovery from intense exercise., in J Strength Cond Res, n. 26, 2012, pp. 80-6.
Bibliografia
[modifica | modifica wikitesto]- David L. Nelson e Michael M. Cox, Lehninger Principles of Biochemistry, New York, W. H. Freeman and company, 2005, pp. 841, ISBN 0-7167-4339-6.
Voci correlate
[modifica | modifica wikitesto]Altri progetti
[modifica | modifica wikitesto] Wikizionario contiene il lemma di dizionario «metabolismo»
Wikizionario contiene il lemma di dizionario «metabolismo» Wikiversità contiene una lezione sul metabolismo
Wikiversità contiene una lezione sul metabolismo Wikimedia Commons contiene immagini o altri file sul metabolismo
Wikimedia Commons contiene immagini o altri file sul metabolismo
Collegamenti esterni
[modifica | modifica wikitesto]- metabolismo, su Treccani.it – Enciclopedie on line, Istituto dell'Enciclopedia Italiana.
- Michele MITOLO e Giuseppe GOLA, METABOLISMO, in Enciclopedia Italiana, Istituto dell'Enciclopedia Italiana, 1934.
- Carlo Alfonso Rossi, METABOLISMO, in Enciclopedia Italiana, III Appendice, Istituto dell'Enciclopedia Italiana, 1961.
- Carlo Alfonso Rossi e Libero Martoni, METABOLISMO, in Enciclopedia Italiana, IV Appendice, Istituto dell'Enciclopedia Italiana, 1979.
- Franca Ascoli, METABOLISMO, in Enciclopedia Italiana, V Appendice, Istituto dell'Enciclopedia Italiana, 1993.
- Domenico Andreani e Nicola Locuratolo, Metabolismo, in Universo del corpo, Istituto dell'Enciclopedia Italiana, 1998-2000.
- EEric A. Newsholme, Bernard Crabtree, Bernard Axelrod e Konrad Bloch, Metabolismo, in Enciclopedia del Novecento, Istituto dell'Enciclopedia Italiana, 1975-2004.
- Metabolismo, in Dizionario di medicina, Istituto dell'Enciclopedia Italiana, 2010.
- Metabolismo, su Vocabolario Treccani, Istituto dell'Enciclopedia Italiana.
- metabolismo, su sapere.it, De Agostini.
- Luisa Minghetti, Metabolismo, in Enciclopedia dei ragazzi, Istituto dell'Enciclopedia Italiana, 2004-2006.
- (EN) Hans Kornberg, metabolism, su Enciclopedia Britannica, Encyclopædia Britannica, Inc.
- (EN) Opere riguardanti Metabolismo, su Open Library, Internet Archive.
| Controllo di autorità | Thesaurus BNCF 7725 · LCCN (EN) sh85084016 · GND (DE) 4057699-1 · BNF (FR) cb119383963 (data) · J9U (EN, HE) 987007565652405171 |
|---|