Ribonucleasi A
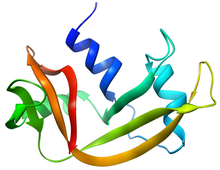
La Ribonucleasi A (RNasi A) fa parte della classe delle endonucleasi, le quali sono in grado di degradare RNA a singolo filamento. La RNasi A pancreatica bovina è uno dei classici sistemi modello della scienza delle proteine.
Storia[modifica | modifica wikitesto]
L'importanza della RNasi A pancreatica bovina fu garantita quando la Armour & Co. (famosa per l'hot dog) ne purificò un chilogrammo, e ne donò campioni da 10 mg a qualunque scienziato fosse interessato. La possibilità di ottenere un singolo lotto di enzima purificato rese immediatamente la RNasi il sistema modello dello studio delle proteine.
La RNasi A fu la proteina modello utilizzata per elaborare molti metodi spettroscopici per determinare la struttura delle proteine, tra cui l'assorbanza, il dicroismo circolare e la dispersione rotatoria, la spettroscopia Raman, risonanza paramagnetica elettronica e la risonanza magnetica nucleare. La RNasi A fu anche il primo modello proteico per lo sviluppo di chimica strutturale, come la proteolisi limitata di segmenti disordinati, modificazione chimica delle catene laterali esposte, e il riconoscimento antigenico.
La ribonucleasi-S, RNasi A trattata con subtilisina, fu la terza proteina la cui struttura fosse risolta, nel 1967.[1]
Studi sul folding ossidativo della RNasi A portò Chris Anfinsen a formulare l'ipotesi termodinamica del ripiegamento delle proteine, il quale postula che la forma ripiegata di una proteina rappresenti il suo stato di minima energia libera.
La RNasi A fu la prima proteina a mostrare gli effetti di isomeri non-nativi dovuti a legami peptidici della X-Pro nel folding delle proteine.
La RNasi A fu la prima proteina ad essere studiata attraverso allineamenti di sequenze multiple e mediante comparazione di proprietà mantenute tra proteine correlate evolutivamente.
Struttura e proprietà[modifica | modifica wikitesto]

La RNasi A è una proteina relativamente piccola (124 residui, ~13.7 kDa). Può essere definita una proteina ripiegata a metà assumendo la forma di un taco, con un profondo solco per il legame con l'RNA substrato. Il primo dominio è formato da tre alpha eliche (residui 3-13, 24-34 e 50-60) dall'N-terminale della proteina. Il secondo dominio consiste in β-hairpins (forcine β) (residui 61-74, 79-104 e 105-124 dalla porzione C-terminale) disposte in due foglietti β. Le forcine beta 61-74 e 105-124 formano un foglietto beta antiparallelo di quattro filamenti che giace sulla alpha elica numero 3 (residui 50-60). La forcina β più lunga (79-104) è associata ad un breve foglietto β (residui 42-45) a formate un foglietto β antiparallelo di tre filamenti, che giace sulla alpha elica 2 (residui 24-34).
La RNasi A contiene quattro ponti disolfuro nella sua forma nativa: Cys26-Cys84, Cys58-110, Cys40-95 e Cys65-72. I primi due (26-84 e 58-110) sono essenziale per il corretto ripiegamento; ciascuno lega una alpha elica del primo filamento ad un foglietto beta del secondo, formando accanto un piccolo core idrofobico. Gli altri due legami disolfuro (40-95 e 65-72) sono meno importanti per il ripiegamento; ciascuno dei due (ma non entrambi contemporaneamente) può essere ridotto senza influire sulla struttura nativa in condizioni fisiologiche. Questi ponti disolfuro collegano segmenti a loop e sono relativamente esposti al solvente. Sorprendentemente, il legame disolfuro 65-72 ha una frequenza di formazione straordinariamente alta, significativamente maggiore di quanto ci si potrebbe aspettare dalla sua loop entropy, sia in quanto peptide che nell'intera proteina. Questo fatto suggerisce che la forcina β 61-74 abbia un'alta propensione a far ripiegare la proteina nella conformazione corretta.
La RNasi A è una proteina basica (pI =8.63); le sue numerose cariche positive favoriscono il legame con l'RNA (un poli-anione). Più in generale, la RNasi A è difficilmente polare, mancando insolitamente di gruppi idrofobici, specialmente in quelli alifatici. Questo può essere la causa della necessità di quattro ponti disolfuro per stabilizzare la struttura.
Il basso contenuto idrofobico può avere anche lo scopo di ridurre la repulsione fisiologica tra gruppi fortemente carichi (i suoi e quelli dell'RNA substrato) e le regioni a bassa costante dielettrica (residui non polari).
L'alpha elica N-terminale della RNasi A (residui 3-13) è connessa al resto della proteina da un linker flessibile (residui 16-23). Come mostrato da F. M. Richards, questo linker può essere tagliato dalla subtilisina tra i residui 20 e 21, senza causare la dissociazione della elica N-terminale dal resto della RNasi A. Il complesso peptide-proteina è chiamato RNasi S, il peptide (residue 1-20) è conosciuto come peptide S e il resto (residui 21-124) è chiamato proteina S. La costante di dissociazione del peptide-S dalla proteina-S è di 30 pM; questo forte legame può essere sfruttato durante la purificazione della proteina legando il peptide S alla proteina di interesse e facendo passare la soluzione su una colonna cromatografica legante la proteina S. [Anche un peptide C più breve (residui 1-13) funziona.] Il sistema modello RNasi S è stato anche utilizzato per studiare il folding della proteina, accoppiando folding associazione. Il peptide S fu il primo peptide di una proteina nativa che mostrò di avere struttura secondaria dinamica quando isolato (by Klee e Brown in 1967).
Meccanismo Enzimatico[modifica | modifica wikitesto]
La carica positiva della RNasi A giace principalmente in un solco profondo tra i due lobi. L'RNA substrato giace in questo solco e viene tagliato da due istidine catalitiche, His12 e His119, attraverso intermedio fosfato 2'-3' ciclico che è stabilizzato dalle lisine vicine, Lys7, Lys41 e Lys66.
Effetto anti-cancerogeno[modifica | modifica wikitesto]
La RNasi A, e in più larga misura i suoi oligomeri e alcuni omologhi (ovvero la onconasi delle rane), possiede effetti citotossici e citostatici, particolarmente sulle cellule tumorali. Questo ha condotto all'uso della onconasi come onco-terapeutici, particolarmente per uso esterno contro il cancro della pelle. Come con altri farmaci proteici, l'uso interno di ribonucleasi non umane come la onconasi è limitata dalla risposta immunitaria del paziente.
Altri effetti biologici[modifica | modifica wikitesto]
La ribonucleasi è anche collegata alla angiogenina, coinvolta nello sviluppo dei vasi sanguigni.
Note[modifica | modifica wikitesto]
- ^ Wyckoff HW, Hardman KD, Allewell NM, Inagami T, Johnson LN e Richards FM, The structure of ribonuclease-S at 3.5 Å resolution [collegamento interrotto], in J. Biol. Chem., vol. 242, n. 17, settembre 1967, pp. 3984–8, PMID 6037556.
Bibliografia[modifica | modifica wikitesto]
- Kartha, G., Bello, J., Harker, D., Tertiary Structure of Ribonuclease, Boston, Nature, 1967, ISBN 0-12-588945-3.
- Raines RT, Ribonuclease A, in Chem. Rev., vol. 98, n. 3, maggio 1998, pp. 1045–66, PMID 11848924.
- Scheraga HA, Wedemeyer WJ, Welker E, Bovine pancreatic ribonuclease A: oxidative and conformational folding studies, in Meth. Enzymol., vol. 341, 2001, pp. 189–221, PMID 11582778.
Voci correlate[modifica | modifica wikitesto]
Collegamenti esterni[modifica | modifica wikitesto]
- (EN) Ribonuclease A, in Medical Subject Headings (MeSH), National Library of Medicine, 2009.
